W latach 70-ych DNA uważano za najtrudniejszą do analizy makrocząsteczkę i mogło być analizowane tylko metodami pośrednimi poprzez analizę białek, sekwencjonowanie RNA itp. Obecnie DNA jest najłatwiejszym materiałem do badań.
Można np. przeciętnie w ciągu 1 dnia wyizolować specyficzny fragment genomu, wyprodukować w laboratorium dowolną ilość jego identycznych kopii, a także określić jego sekwencję dosłownie przez 1 noc. W oparciu o podobne techniki taki wyizolowany gen można zmienić (np. wprowadzając mutacje) i wprowadzić ponownie do dowolnych komórek w taki sposób, by funkcjononował w zgodzie z pozostałymi mechanizmami komórkowymi i umożliwiał analizę wprowadzonych zmian na poziomie komórkowym, tkankowym, organu bądź całego organizmu.
Techniki rekombinacji DNA są obecnie podstawowymi technikami BIOLOGII KOMÓRKI i umożliwiają poznanie tak komórek jak i budujących je makrocząsteczek na tysiące wręcz sposobów. Te same techniki umożliwiają produkcję na szeroką skalę np. białek, hormonów i szczepionek. Ponadto, ponieważ jest możliwa analiza regulatorowych regionów genów (promotorów), pozwala to biologom analizować szereg nieraz bardzo skomplikowanych mechanizmów regulacji genów u wyższych organizmów.
Podstawowe techniki analizy i inżynierii DNA/RNA obejmują:
Cięcie DNA w specyficznych miejscach przez ENZYMY RESTRYKCYJNE
Klonowanie DNA z użyciem odpowiednich wektorów oraz PCR, w wyniku czego pojedynczy fragment cząsteczki DNA może być użyty do otrzymania bilionów identycznych cząsteczek
Hybrydyzację kwasów nukleinowych, pozwalającą znaleźć odpowiednią sekwencję DNA lub RNA z dużą dokładnością, w oparciu o wiązanie komplementarnych sekwencji DNA lub RNA
Sekwencjonowanie wszystkich nukleotydów w oczyszczonej próbce DNA, co pozwala zidentyfikować geny, a także wydedukować sekwencję aminokwasów dla białka, które kodują
Monitorowanie ekspresji wielu genów w komórce z użyciem tzw. macierzy DNA (z ang. „microarrays”) itp. narzędzi, które pozwalaja dokonać tysięcy hybrydyzacji równocześnie
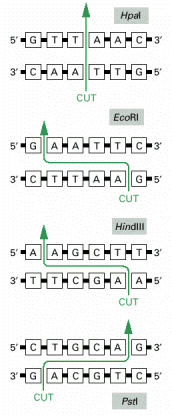
ENZYMY RESTRYKCYJNE: Mogą być wyizolowane i oczyszczone np. z bakterii, różne szczepy bakterii produkują różne enzymy restrykcyjne. Enzymy te chronią bakterie przed wirusami degradując wirusowe DNA i mają wysoką specyficzność, tj różne enzymy tną podwójną helisę DNA w różnych miejscach. Rozpoznają one specyficzną sekwencję 4-8 nukletydów obcego DNA. Własne DNA bakterii jest chronione przed działaniem ich własnych enzymów restrykcyjnych poprzez metylację zasad A i C we własnym DNA.
Pochodzenie enzymów na rusunku obok: HpaI: Hemophilus parainfluenzae, EcoRI: Escherichia coli, HindIII: Hemophilus influenzae, PstI: Providencia stuartii.
Enzymy restrykcyjne tną nić DNA albo w danym miejscu, albo w pobliżu określonej sekwencji i zwykle tną DNA tak, że pozostawiają tzw. „lepkie końce”, czyli wystające jednoniciowe fragmenty DNA po obu stronach rozpoznawanej sekwencji. W niektórych przypadkach tną jednak nić tak, że pozostawiają tzw. „tępe końce”, jak np. HpaI
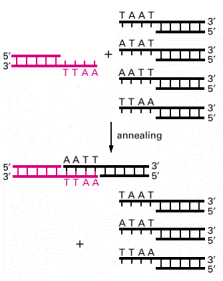
Fragmenty DNA posiadające identyncze lepkie końce mogą być łatwo dopasowane, jak pokazuje to rysunek poniżej, tępe końce można również połaczyć z odpowiednim DNA, choć wymaga to więcej pracy.
Połączone ze sobą dwa lub więcej fragmenty DNA powszechnie nazywane jest rekombinowanym DNA
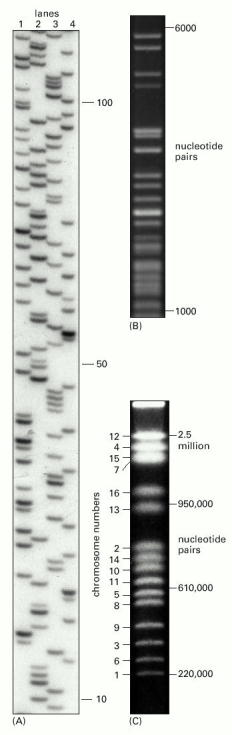
ROZMIAR (długość) fragmentu DNA służy zwykle do rozpoznania interesującego nas fragmentu w mieszaninie pociętych fragmentów DNA.
ELEKTROFOREZA DNA: Opiera się na podobnych zasadach jak elektroforeza białek. W przypadku DNA jest ona jeszcze prostsza, ponieważ DNA jest naładowane ujemnie i nie trzeba nadawać mu ładunku ujemnego jak w przypadku białek z użyciem SDS.
Na załączonym rysunku użyto dla A: żelu poliakrylamidowego o małych porach do frakcjonowania fragmentów (10-500 nukleotydów) jednoniciowego DNA , dla B: żelu agarozowego o średniej wielkości porów dla frakcjonowania średniej wielkości fragmentów dwuniciowego DNA (300-10 000 nukleotydów), a dla C: zastosowano tzw. „pulsed-field agarose gel electrophoresis” do rozdzielenia fragmentów DNA 220 000 - 2.5 mln nukleotydów.
Ostatnia z wymienionych metod polega na rozdziale dużych cząsteczek DNA w polu elektrycznym, którego kierunek zmieniany jest okresowo. W stałym polu elektrycznym takie duże cząsteczki nie mogłyby być rozdzielone.
W przypadku B i C detekcję DNA w żelu przeprowadzono barwiąc żel bromkiem etydyny, który wbudowuje się w DNA, podświetlając żel następnie światłem UV. W przypadku A zastosowano odpowiednie znakowanie izotopowe (tj 32P; patrz: sekwencjonowanie metodą Sangera).
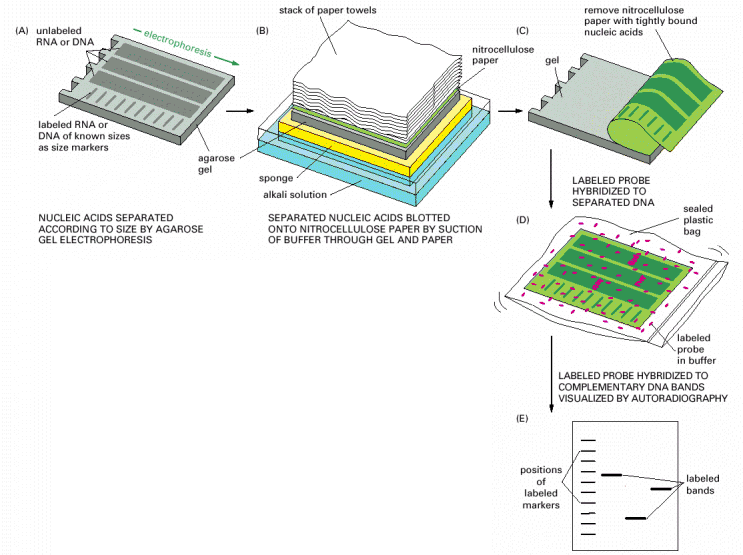
NORTHERN i SOUTHERN BLOT to sposób transferu RNA i DNA na odpowiednie filtry, które ułatwiają detekcję interesujących nas fragmentów RNA lub DNA za pomocą odpowiednich SOND i metod hybrydyzacji DNA/DNA, RNA/RNA oraz RNA/DNA
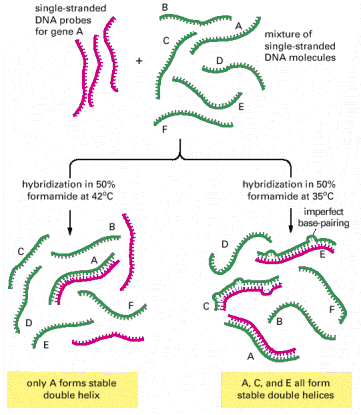
HYBRYDYZACJA: Kiedy roztwór wodny DNA jest podgrzany do temperatury 100°C lub poddany działaniu wysokiego pH (pH ≥ 13) komplementarne zasady DNA dysocjują, pozwalając na rozdzielenie dwuniciowego DNA na pojedyncze nici. Proces ten nazywany jest DENATURACJĄ DNA. Jeśli takie zdenaturowane DNA podgrzeje się ponownie w temperaturze 65°C następuje renaturacja DNA lub inaczej hybrydyzacja DNA do formy podwójnej helisy. Hybrydyzacja może zachodzić pomiędzy komplementarnymi fragmentami DNA, RNA i DNA, oraz RNA i RNA.
Jednoniciowe fragmenty DNA lub RNA komplementarnego do odpowiednij sekwencji stanowiącej matrycę nazywa się SONDAMI. Umożliwiają one detekcję wybranego fragmentu kwasu nukleinowego poprzez znakowanie ich izotopowo lub chemicznie. Hybrydyzacja jest tak selektywna, czuła i specyficzna, że pozwala wykryć nawet jedną cząsteczkę określonego fragmentu w komórce.
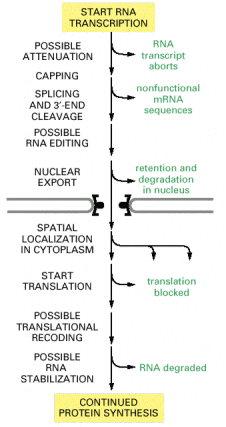
W oparciu o hybrydyzację RNA i DNA można badać nie tylko, czy zachodzi ekspresja danego genu w komórkach, ale również jakiego rodzaju modyfikacjom podlega ten fragment w ramach mechanizmów kontroli w trakcie i po transkrypcji DNA do mRNA
Klasycznego transferu DNA i RNA na odpowiednie filtry nie trzeba dokonywać w aparacie jak w przypadku białek, a jedynie użyć metody kapilarnej przedstawionej poniżej
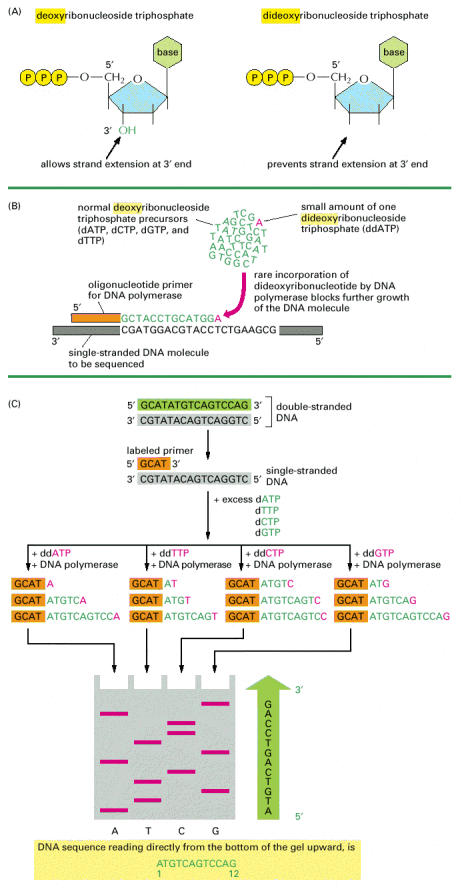
SEKWENCJONOWANIE DNA:
W późnych latach 70-ych opracowano technikę sekwencjonowania DNA z wykorzystaniem tzw. didioxy pochodnych nukleotydów.
Jak się znajduje region DNA faktycznie kodujący jakieś białko?
Dowolny region DNA może kodować jakieś białko i zwykle musimy rozważyć 6 różnych kombinacji sekwencji, ponieważ mamy do dyspozycji 2 nici DNA i na każdej 3 ramki odczytu (gdyż kod genetyczny jest 3-literowy). Ustalono regułę, że sekwencję nukleotydów czyta się zawsze od 5' do 3' i wówczas odpowiadająca im sekwencja aminokwasów czytana będzie od N-końca do C-końca białka. Dla każdego odczytu oszacowuje się częstotliwość występowania kodonu STOP, jeśli dana sekwencja koduje jakieś białko, sygnał STOP nie będzie zdarzał się częściej niż co 21 aminokwasów (czyli raz na 63 nukleotydy).
PCR (Polymerase Chain Reaction): W metodzie tej dwa zestawy oligonukleotydów (tzw. starterów, albo z ang. „primers”) syntetyzuje się z użyciem metod chemicznych tak, by były komplementarne do początku i końca sekwencji, którą chcemy powielić (zamplifikować). Oligonukleotydy te są następnie wykorzystywane do cyklicznych reakcji PCR przeprowadzanych przez specjalną, odporną na zmiany temperatury polimerazę DNA. Reakcje te przeprowadzane są w odpowiednich probówkach laboratoryjnych - obecnie z użyciem aparatów PCR, które umożliwiają nic innego, a po prostu szybkie zmiany temparatur w zakresie od ok. 40 - 100°C
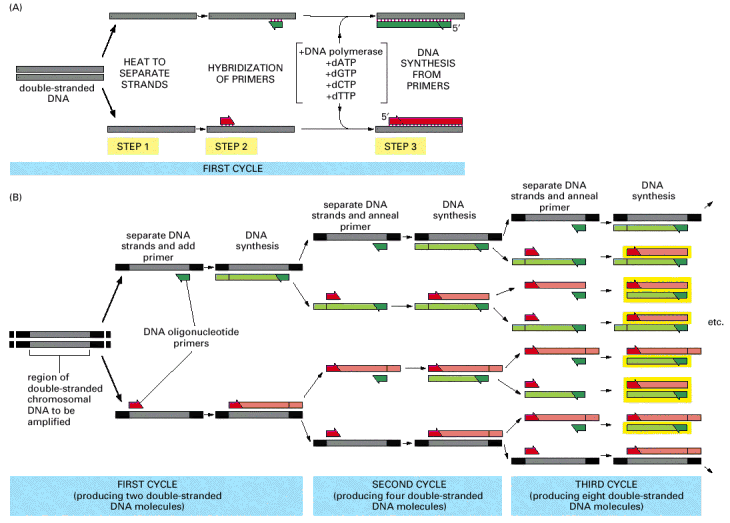
Zwykle 20-30 cyklicznych zmian temparatur wystarczy, by efektywnie powielić dany fragment, a najnowocześniejsze aparaty PCR pozwalaja na przeprowadzenie tych reakcji w przeciągu 1-2 godzin.
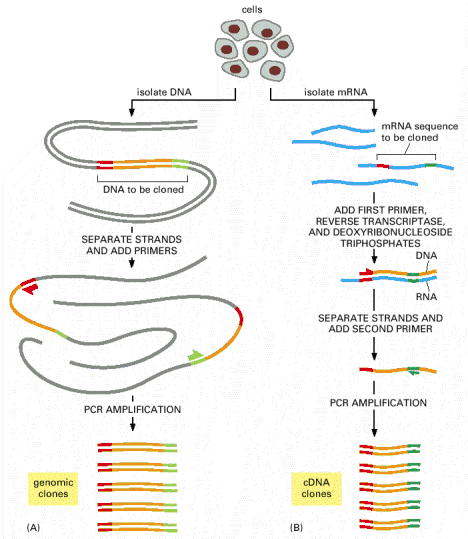
Różnice pomiędzy klasycznym PCR, w którym materiałem wyjściowym jest DNA a RT-PCR, w którym materiałem wyjściowym jest RNA pokazane są na rysunku po lewej.
Poniższa tabela podsumowuje najważniejsze wydarzenia dotyczące rozwoju technik rekombinacji DNA i tworzenia organizmów transgenicznych.
Some Major Steps in the Development of Recombinant DNA and Transgenic Technology |
|
|
|
1869 |
Miescher first isolates DNA from white blood cells harvested from pus-soaked bandages obtained from a nearby hospital. |
1944 |
Avery provides evidence that DNA, rather than protein, carries the genetic information during bacterial transformation. |
1953 |
Watson and Crick propose the double-helix model for DNA structure based on x-ray results of Franklin and Wilkins. |
1955 |
Kornberg discovers DNA polymerase, the enzyme now used to produce labeled DNA probes. |
1961 |
Marmur and Doty discover DNA renaturation, establishing the specificity and feasibility of nucleic acid hydridization reactions. |
1962 |
Arber provides the first evidence for the existence of DNA restriction nucleases, leading to their purification and use in DNA sequence characterization by Nathans and H. Smith. |
1966 |
Nirenberg, Ochoa, and Khorana elucidate the genetic code. |
1967 |
Gellert discovers DNA ligase, the enzyme used to join DNA fragments together. |
1972-1973 |
DNA cloning techniques are developed by the laboratories of Boyer, Cohen, Berg, and their colleagues at Stanford University and the University of California at San Francisco. |
1975 |
Southern develops gel-transfer hybridization for the detection of specific DNA sequences. |
1975-1977 |
Sanger and Barrell and Maxam and Gilbert develop rapid DNA-sequencing methods. |
1981-1982 |
Palmiter and Brinster produce transgenic mice; Spradling and Rubin produce transgenic fruit flies. |
1982 |
GenBank, NIH's public genetic sequence database, is established at Los Alamos National Laboratory. |
1985 |
Mullis and co-workers invent the polymerase chain reaction (PCR). |
1987 |
Capecchi and Smithies introduce methods for performing targeted gene replacement in mouse embryonic stem cells. |
1989 |
Fields and Song develop the yeast two-hybrid system for identifying and studying protein interactions |
1989 |
Olson and colleagues describe sequence-tagged sites, unique stretches of DNA that are used to make physical maps of human chromosomes. |
1990 |
Lipman and colleagues release BLAST, an algorithm used to search for homology between DNA and protein sequences. |
1990 |
Simon and colleagues study how to efficiently use bacterial artificial chromosomes, BACs, to carry large pieces of cloned human DNA for sequencing. |
1991 |
Hood and Hunkapillar introduce new automated DNA sequence technology. |
1995 |
Venter and colleagues sequence the first complete genome, that of the bacterium Haemophilus influenzae. |
1996 |
Goffeau and an international consortium of researchers announce the completion of the first genome sequence of a eucaryote, the yeast Saccharomyces cerevisiae. |
1996-1997 |
Lockhart and colleagues and Brown and DeRisi produce DNA microarrays, which allow the simultaneous monitoring of thousands of genes. |
1998 |
Sulston and Waterston and colleagues produce the first complete sequence of a multicellular organism, the nematode worm Caenorhabditis elegans. |
2001 |
Consortia of researchers announce the completion of the draft human genome sequence. |
BIOLOGIA KOMÓRKI; 11-15 STYCZNIA 2010
Podstawy ANALIZY KWASÓW NUKLEINOWYCH
Wyszukiwarka
Podobne podstrony:
05 Geoelektryka02 SP 2id 5953 ppt
5953
5953
5953
5953
więcej podobnych podstron