
METODY
DIAGNOSTYCZNE
OPARTE NA
POLIMORFIZMIE
DNA
Aneta Włodarczyk

1.Struktura ludzkiego genomu
Genom to kompletny zestaw informacji
genetycznej zawartej w DNA komórki,
zawiera program genetyczny dzięki
któremu komórka wie jak funkcjonować.
Genom człowieka zbudowany jest z około
3,2∙10
9
nukleotydów .
Całkowita liczba genów u człowieka
wynosi 30 000 genów.
Genom ludzki rozdzielony jest na 22
autosomy i 2 chromosomy płciowe.
Sekwencja genomu człowieka zawarta
jest w 24 chromosomach.
2

Chromosom jest zbudowany z DNA i
białek, z których największą masę
stanowią histony. Histony
odznaczają się zwiększoną, w
porównaniu z innymi białkami,
liczba aminokwasów zasadowych,
takich jak lizyna czy arginina, co
ułatwia im wiązanie się z DNA. Po
dwa histony H2A, H2B, H3 oraz H4
tworzą specyficzny oktamer w
kształcie walca na który „nawinięty”
jest DNA tworząc nukleosom.
Kompleks kwasy nukleinowe –
białka nazywany jest chromatyną.
3

Poza białkami oktameru rdzeniowego
istnieje grupa dodatkowych histonów,
tzw. histony łącznikowe który działa
jak klamra zapobiegająca oddzieleniu
się DNA od kompleksu.
Chromosomy jako indywidualne
struktury są widoczne tylko podczas
podziału komórkowego. Stanowią one
specyficzną formę wielostopniowej
organizacji przestrzennej chromatyny.
4

Chromosomy metafazowe czyli
najbardziej skondensowana postać
chromatyny zbudowane są z dwóch
identycznych chromatyd. Miejsce
polaczenia chromatyd – centromer
dzieli chromosom na dwa ramiona,
krótkie i długie. Regiony na
końcach obu ramion nazywane są
telomerami.
5
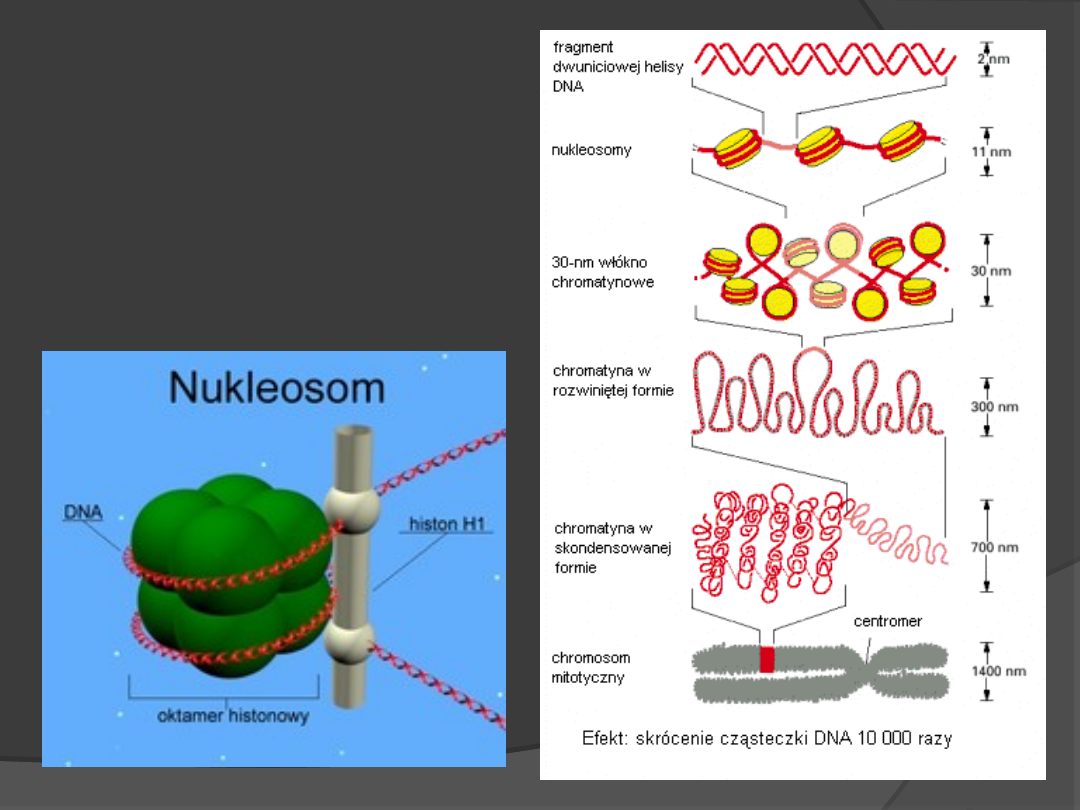
Struktura
upakowania
DNA w
komórce
6

Odcinki kodujące stanowią tylko 1-
3% całego genomu.
Około 30% stanowią sekwencje
ulegające transkrypcji oraz
sekwencje związane z genami.
Pozostała część genomu to różne
klasy sekwencji powtórzonych oraz
sekwencje unikatowe.
7

Ciekawostki
Zapis sekwencji całego genomu
człowieka zająłby ponad tysiąc
tomów książki o dużych
rozmiarach.
Zamknięcie całego DNA w jądrze
komórki można porównać do próby
zwinięcia 40 km niezmiernie
cienkiej nici do rozmiarów piłki
tenisowej.
8

Gdybyśmy każdą parę nukleotydów
narysowali tak , że zajęłaby 1mm, to
genom człowieka rozciągnąłby się na
długość 3200 km, która odpowiada
szerokości Afryki Centralnej. W tej skali
gen kodujący białko występowałby co
300 m, a sekwencja kodująca
zajmowałaby 1m.
Genomy ludzkie różnią się średnio
jednym nukleotydem na 1000. To
zróżnicowanie decyduje o naszych
indywidualnych cechach i stanowi
podstawę identyfikacji osób z
zastosowaniem DNA.
9

Genom człowieka
Genom jądrowy zlokalizowany w jądrze
komórkowym.
- zbudowany z około 3 miliardów par zasad,
- złożony z 24 różnych dwuniciowych liniowych
cząsteczek DNA – chromosomów,
Genom mitochondrialny obecny w
mitochondriach.
- zbudowany z około 16 kbp (dużo mniejszy niż
genom jądrowy),
- kolista dwuniciowa cząsteczka DNA,
- obecny we wszystkich mitochondriach, w
wielu kopiach w komórce,
10

Genom jądrowy
DNA genowy (30%)- geny i
sekwencje związane z genami to:
eksony, introny, pseudogeny,
fragmenty genów, sekwencje
regulatorowe, sekwencje
początkowe i końcowe genów.
DNA pozagenowy (70%)-
sekwencje unikatowe oraz
sekwencje powtórzone.
11

DNA genowy
Sekwencje kodujące .
Sekwencje niekodujace :
Fragmenty genów,
Introny,
Pseudogeny – sekwencje DNA bardzo
podobne do genów funkcjonalnych, ale
zawierające liczne mutacje,
uniemożliwiające ich prawidłową ekspresję,
Sekwencje regulatorowe,
Sekwencje początkowe i końcowe genów,
12

DNA pozagenowy
Sekwencje unikatowe -
głównie geny
struktury (białek i RNA) oraz pseudogeny.
Sekwencje powtórzone:
Sekwencje tandemowe – sekwencje
ułożone obok siebie w bloki o długości
kilku tysięcy par zasad.
Sekwencje rozproszone – poszczególne
krótkie powtarzające się elementy liczące
100-300 par zasad są oddzielone od
siebie innymi sekwencjami. Powtarzalność
rzędu 10
4
-10
5
razy.
13

Sekwencje tandemowe
0,5 – 20% ogólnej ilości DNA
satelitarne –
większość powtórzeń
występuje w regionach centromerowych
chromosomu, odgrywając tam prawdopodobnie
funkcje strukturalną, ilość powtarzających się
sekwencji w genomach różnych organizmów ,
jak i ich powtarzalność stanowi
charakterystyczną cechę danego organizmu.
minisatelitarne
– fragmenty długości
sięgającej 20 kbp, z powtarzającą się jednostką
długości około 25 bp; występują najczęściej w
telomerach lub w pobliżu końców chromosomu;
funkcja nieznana.
14

mikrosatelitarne –
powtórzenia krótkie,
zwykle poniżej 150 bp, a jednostka
powtórzona to 1-, 2-, 3-, 4 pary zasad;
funkcja nieznana. Powtórzenia tego typu
znalazły zastosowanie jako marker
molekularny (np. ustalanie profilu
genetycznego – kryminalistyka).
15

Sekwencje rozproszone
długie LINE (21% genomu) (ang. long
interspersed nuclear element) długie
rozproszone sekwencje jądrowe o
długości około 6,4 kb. Najbardziej
znana to sekwencja LINE-1
krótkie SINE (13% genomu) (ang. short
interspersed nuclear element) - krótkie
rozproszone sekwencje jądrowe –
sekwencje o długości około 100-400
bp. Najbardziej znana to sekwencja
Alu.
16

Transpozony – segment DNA, który może
się przemieszczać w chromosomie z
jednego miejsca na drugie lub z jednego
chromosomu do drugiego w tej samej
komórce. Ważne źródło genetycznej
zmienności u większości organizmów.
Retrotranspozon – rodzaj ruchomego
elementu genetycznego, który
przemieszcza się w genomie w ten
sposób, że najpierw ulega transkrypcji na
RNA, który odwrotna transkryptaza
przekształca na DNA i wprowadza do
genomu w innym miejscu.
Transpozony i retrotranspozony razem
stanowią 3% genomu ludzkiego
17

2. Typy polimorfizmów
DNA
Minisatelitarny VNTR (variable
numer tandem repeats)
Mikrosatelitarny STR (short tandem
repeats)
SNP (single nucleotide
polymorphism)
18

Polimorfizm DNA
Zróżnicowanie genetyczne warunkujące
zmienność wewnątrz gatunku, które można
obserwować na poziomie całego osobnika
(różnice fenotypowe), na poziomie
biochemicznym (np. różne formy antygenów
powierzchniowych komórki, grup krwi,
enzymów ), na poziomie chromosomowym
(różnice cech morfologicznych chromosomów)
oraz na poziomie DNA .
Termin polimorfizm DNA odnosi się do
szerokiego zakresu zmienności pojedynczych
nukleotydów lub powtórzeń nukleotydowych.
19

Polimorfizm DNA występuje powszechnie z
częstością większą niż ogólna częstość
mutacji i to jest kryterium odróżniające
zmianę polimorficzną od mutacji. Przyjmuje
się, że jeżeli w populacji zmiana sekwencji
nukleotydów występuje częściej niż 1 % to
jest to polimorfizm. Większość polimorfizmów
nie wpływa na cechy kliniczne fenotypu i nie
prowadzi do objawów chorobowych.
Sekwencje polimorficzne mogą występować w
sekwencjach kodujących ale głównie obecne
są w nie kodujących regionach DNA.
20

Zastosowania
jako markery genetyczne do śledzenia
sposobu dziedziczenia się choroby w
rodzinie, która sprzężona jest z
określonym markerem genetycznym,
czyli do mapowania genów,
w sądownictwie i kryminalistyce - do
identyfikacji osobniczej oraz ustalania
pokrewieństwa,
do określania genetycznej zgodności
krwi, nasienia czy tkanki.
21

Polimorfizm sekwencji
minisatelitarnych-VNTR
Minisatelity to tandemy DNA zawierające od
10 do 100 nukleotydów , które powtarzają
się w pojedynczym locus od 2 do kilkuset
razy. Mogą występować w jednym albo też
w kilku różnych miejscach genomu.
Zmienność genetyczna wyrażona jest ilością
powtórzeń minisatelitów w danym regionie i
określana jest jako VNTR .
VNTR-y wykrywa się konwencjonalną
metodą RFLP z użyciem sondy molekularnej
komplementarnej do badanego minisatelity.
22

Przykładowy motyw powtórzeń
sekwencji minisatelitarnej może
mieć postać; AGGGCTGGAGG
AGGGCTGGAGG
AGGGCTGGAGG
A
GGGCTGGAGG
AGGGCTGGAGG
A
GGGCTGGAGG
AGGGCTGGAGG…
23

Polimorfizm sekwencji
mikrosatelitarnych –STR
Mikrosatelity to sekwencje
tandemowe, w których motyw 1, 2, 3 i
4 nukleotydowy powtarza się w
pojedynczym locus od kilku do kilkuset
razy. Mikrosatelity rozłożone są mniej
więcej równomiernie co 6 – 10 tysięcy
par zasad w miejscach niekodujących,
jak również w obrębie genów . Ilość
powtórzeń mikrosatelitarnych różni się
znacząco u poszczególnych osób.
24

Polimorfizmy powtórzeń
mikrosatelitarnych nie są wykrywane
metodą RFLP, ponieważ miejsca
cięcia enzymów restrykcyjnych nie
ograniczają rejonu powtórzeń.
Identyfikowane są natomiast techniką
polimerazowej reakcji łańcuchowej
PCR, która to metoda pozwala na
szybką produkcję milionów kopii
krótkich sekwencji DNA.
25

Przykładowy motyw powtórzeń
sekwencji mikrosatelitarnej może
mieć postać; CATA
CATA
CATA
CATA
CATA
CATA
CATA
CA
TA
CATA
CATA
CATA
CATA
CATA…..
26

Polimorfizm pojedynczych
nukleotydów - SNP
Ten typ zmienności polega na występowaniu
zmiany pojedynczych nukleotydów w DNA.
Wykrywany jest, powszechnie stosowaną
metodą, analizy restrykcyjnej fragmentów RFLP
w izolowanym DNA badanego pacjenta przy
użyciu enzymów restrykcyjnych. Metoda RFLP
nie wykrywa rodzaju mutacji punktowej, lecz
wskazuje na obecność zmiany w badanym
regionie DNA. W genomie człowieka wykryto
tysiące miejsc polimorficznych SNP. Ponieważ
SNP występują w tak znaczącej liczbie, stanowią
użyteczne markery do analiz genetycznych.
27
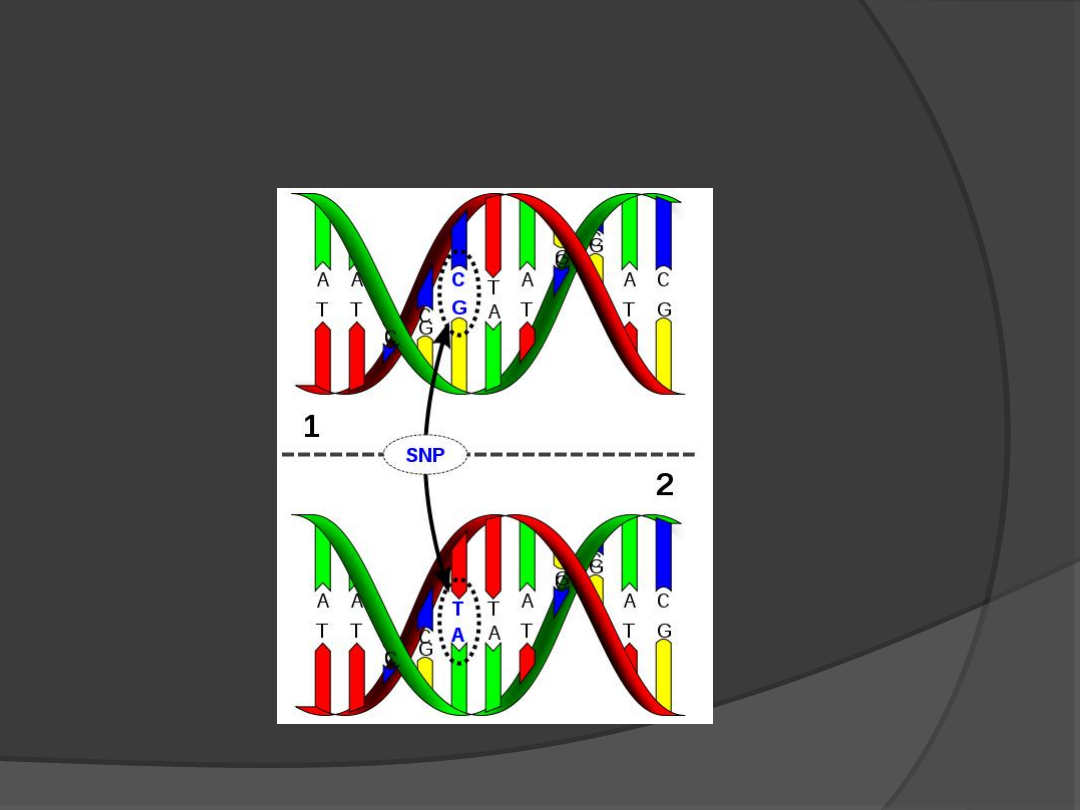
Polimorfizm pojedynczych
nukleotydów - SNP
28

Literatura
Biologia molekularna w
medycynie / J. Bal, PWN (2006)
Biologia molekularna – krótkie
wykłady / P. Turner A. Mc Lenna
A. Bates M. White / PWN (2005)
Podstawy biologii komórki / B.
Alberts, PWN (2005)
29
Document Outline
- Slide 1
- 1.Struktura ludzkiego genomu
- Slide 3
- Slide 4
- Slide 5
- Struktura upakowania DNA w komórce
- Slide 7
- Ciekawostki
- Slide 9
- Genom człowieka
- Genom jądrowy
- DNA genowy
- DNA pozagenowy
- Sekwencje tandemowe 0,5 – 20% ogólnej ilości DNA
- Slide 15
- Sekwencje rozproszone
- Slide 17
- 2. Typy polimorfizmów DNA
- Polimorfizm DNA
- Slide 20
- Zastosowania
- Polimorfizm sekwencji minisatelitarnych-VNTR
- Slide 23
- Polimorfizm sekwencji mikrosatelitarnych –STR
- Slide 25
- Slide 26
- Polimorfizm pojedynczych nukleotydów - SNP
- Polimorfizm pojedynczych nukleotydów - SNP
- Literatura
Wyszukiwarka
Podobne podstrony:
Metody oparte na działalności praktycznej, Ratownicto Medyczne, Metodyka nauczania pierwszej pomocy,
genetyka, ćw 6 geny, 6 Techniki oparte na PCR do diagnozowania chorów genetycznych i uchwycenia zmie
Metody terapii autyzmu oparte na faktach, Metody terapii autyzmu oparte na faktach
Finanse Wycena przedsiębiorstw Metody oparte na zdyskontowanych przepływach (str 6)
Metody rekrutacji i selekcji oparte na kompetencjach
metody oparte na hybrydyzacji
Metody oparte na obserwacji
Metody badania polimorfizmu DNA
Finanse Wycena przedsiębiorstw Metody oparte na zdyskontowanych przepływach (str 6)
T 3[1] METODY DIAGNOZOWANIA I ROZWIAZYWANIA PROBLEMOW
Techniki wywierania wplywu oparte na dynamice interakcji
Metody diagnozy psychologicznej
METODYKA PROWADZENIA ZAJEC NA KURSACH ZEGLARSKICHv 1 1
Przykladowy wywiad obrazujacy prace z oporem, Wywiad psychologiczny i jakościowe metody diagnostyczn
4.1.2 Fale sinusoidalne i prostokątne, 4.1 Wprowadzenie do testowania kabli opartego na częstotliwoś
Informacje zwrotne, Wywiad psychologiczny i jakościowe metody diagnostyczne
METODY DIAGNOSTYKI SKORY, Kosmatologia
więcej podobnych podstron